Konzentration <- c(17.6, 19.2, 21.3, 15.1, 17.6, 18.9, 16.2, 18.3, 19.0, 16.4)52 Lösungen Konfidenzintervalle (eine Stichprobe)
Hier finden Sie die Lösungen zu den Übungsaufgaben von Abschnitt 44.8.
Die hier vorgestellten Lösungen stellen immer nur eine mögliche Vorgehensweisen dar und sind sicherlich nicht der Weisheit letzter Schluss. In R führen viele Wege nach Rom, und wenn Sie mit anderem Code zu den richtigen Ergebnissen kommen, dann ist das völlig in Ordnung.
52.1 Lösung zur Aufgabe 44.8.1
Konzentration.
d <-t.test(Konzentration, mu=0, conf.level=0.95)
d
One Sample t-test
data: Konzentration
t = 31.78, df = 9, p-value = 1.485e-10
alternative hypothesis: true mean is not equal to 0
95 percent confidence interval:
16.68158 19.23842
sample estimates:
mean of x
17.96 # nur Konfidenzintervall ausgeben
as.numeric(d$conf.int)[1] 16.68158 19.23842d <-t.test(Konzentration, mu=0, conf.level=0.99)
d
One Sample t-test
data: Konzentration
t = 31.78, df = 9, p-value = 1.485e-10
alternative hypothesis: true mean is not equal to 0
99 percent confidence interval:
16.1234 19.7966
sample estimates:
mean of x
17.96 # nur Konfidenzintervall ausgeben
as.numeric(d$conf.int)[1] 16.1234 19.7966Mit höherem Konfidenzniveau sinkt die Genauigkeit der Aussagen.
# Berechnung der Standardabweichung der Stichprobe
sigma <- sd(Konzentration)
# Gegebene Werte
# z-Wert für 95% Konfidenzniveau
z <- 1.96
# Fehlermarge
E <- 0.5
# Berechnung der Stichprobengröße
n <- (z * sigma / E)^2
# Aufrunden auf die nächste ganze Zahl
ceiling(n) [1] 50t.test(Konzentration, mu = 16, alternative = "greater")
One Sample t-test
data: Konzentration
t = 3.4682, df = 9, p-value = 0.003534
alternative hypothesis: true mean is greater than 16
95 percent confidence interval:
16.92404 Inf
sample estimates:
mean of x
17.96 Der Test ist signifikant. Wir können also sagen, dass unserer Medikamentencharge wirksam ist.
52.2 Lösung zur Aufgabe 44.8.2
Hof und Fett.
# Daten übertragen
Hof1 <- data.frame(Fett = c(0.34, 0.34,
0.32, 0.35,
0.33, 0.33,
0.32, 0.32,
0.33, 0.30,
0.31, 0.32))
Hof1$Hof <- "Hof 1"
Hof2 <- data.frame(Fett = c(0.28, 0.29,
0.30, 0.32,
0.32, 0.31,
0.29, 0.29,
0.31, 0.32,
0.29, 0.31,
0.33, 0.32,
0.32, 0.33))
Hof2$Hof <- "Hof 2"
milch <- rbind(Hof1, Hof2)
milch$Hof <- factor(milch$Hof)t.test(milch$Fett, conf.level=0.95)
One Sample t-test
data: milch$Fett
t = 96.537, df = 27, p-value < 2.2e-16
alternative hypothesis: true mean is not equal to 0
95 percent confidence interval:
0.3090040 0.3224246
sample estimates:
mean of x
0.3157143 t.test(Hof1$Fett, conf.level=0.95)
One Sample t-test
data: Hof1$Fett
t = 81.853, df = 11, p-value < 2.2e-16
alternative hypothesis: true mean is not equal to 0
95 percent confidence interval:
0.3170719 0.3345948
sample estimates:
mean of x
0.3258333 t.test(Hof2$Fett, conf.level=0.95)
One Sample t-test
data: Hof2$Fett
t = 76.994, df = 15, p-value < 2.2e-16
alternative hypothesis: true mean is not equal to 0
95 percent confidence interval:
0.299595 0.316655
sample estimates:
mean of x
0.308125 # Vorbereitung
h1 <- t.test(Hof1$Fett, conf.level=0.95)
h2 <- t.test(Hof2$Fett, conf.level=0.95)
# Als Datenframe für ggplot zusammenbauen
df <- data.frame(unten = c(h1$conf.int[1], h2$conf.int[1]),
oben = c(h1$conf.int[2], h2$conf.int[2]),
mitte = c(h1$estimate, h2$estimate ),
Hof = c("Hof 1", "Hof 2"))
# ggplot
ggplot(df, aes(x=Hof, color=Hof)) +
geom_point(aes(y=mitte)) +
geom_segment(aes(xend=Hof, y=unten, yend=oben))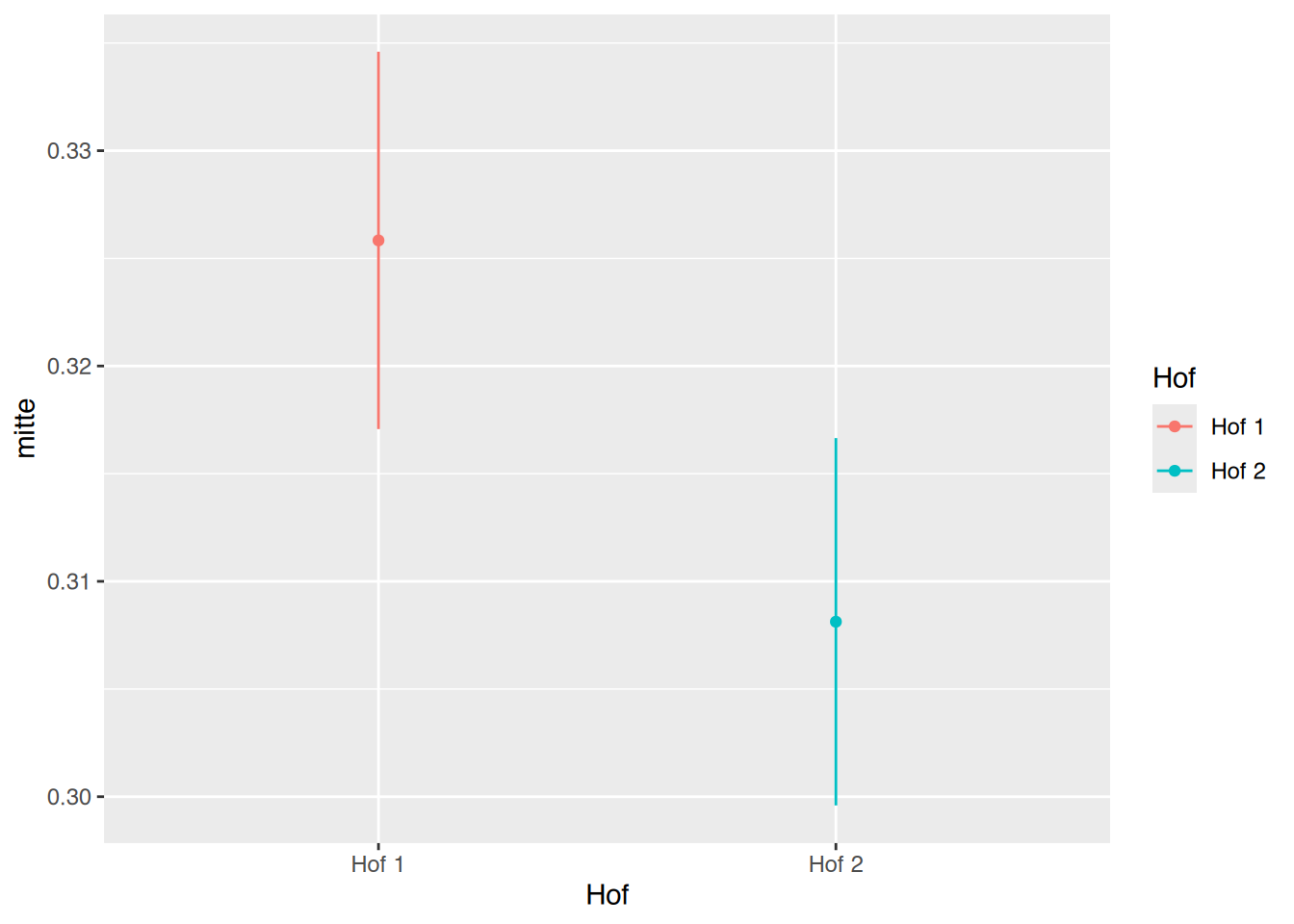
df unten oben mitte Hof
1 0.3170719 0.3345948 0.3258333 Hof 1
2 0.2995950 0.3166550 0.3081250 Hof 2Die beiden Konfidenzintervalle überschneiden sich nicht. Das heisst, es kann ein signifikanter Unterschied abgeleitet werden.
52.3 Lösung zur Aufgabe 44.8.3
Antwort.
# Daten übertragen
Antwort <- c("nein", "ja", "nein", "nein", "nein", "ja", "nein",
"ja", "ja", "ja", "ja", "nein", "ja", "nein", "ja",
"nein", "nein", "nein", "ja", "ja", "ja", "nein",
"nein", "ja", "nein", "nein", "ja", "ja", "nein",
"nein", "ja", "nein", "ja", "nein")freq <- table(Antwort)
bib <- prop.test(freq[["ja"]], sum(freq),
alternative="two.sided",
p=0.5, conf.level=0.99)
bib
1-sample proportions test with continuity correction
data: freq[["ja"]] out of sum(freq), null probability 0.5
X-squared = 0.029412, df = 1, p-value = 0.8638
alternative hypothesis: true p is not equal to 0.5
99 percent confidence interval:
0.2617050 0.6896622
sample estimates:
p
0.4705882 bib$conf.int[2] - bib$conf.int[1][1] 0.4279572Das Intervall ist sehr breit und daher unpräzise.
# gemessene Proportionen
prop <- bib$estimate
# Z-Wert für 95% Konfidenz
z <- 1.96
# Fehlerspanne +-1%
e <- 0.01
# Fallzahl berechnen
n <- (z^2 * prop * (1 - prop)) / (e^2)Es werden 9571 Probanden benötigt.
52.4 Lösung zur Aufgabe 44.8.4
# Daten übertragen
prop.test(154, 200, p=0.5, conf.level=0.95)
1-sample proportions test with continuity correction
data: 154 out of 200, null probability 0.5
X-squared = 57.245, df = 1, p-value = 3.848e-14
alternative hypothesis: true p is not equal to 0.5
95 percent confidence interval:
0.7042503 0.8251428
sample estimates:
p
0.77 # Daten übertragen
prop.test(154, 200, p=0.5, conf.level=0.95)$conf.int[1][1] 0.7042503Da die untere Grenze des Konfidenzintervalls größer als 0,7 ist, können wir bestätigen, dass das Ministerium sein Ziel erreicht hat.
52.5 Lösung zur Aufgabe 44.8.5
# Daten übertragen
cholesterin <- c(196, 212, 188, 206, 203, 210, 201, 198)
t.test(cholesterin, conf.level=0.90)
One Sample t-test
data: cholesterin
t = 72.849, df = 7, p-value = 2.416e-11
alternative hypothesis: true mean is not equal to 0
90 percent confidence interval:
196.5031 206.9969
sample estimates:
mean of x
201.75 t.test(cholesterin, conf.level=0.95)
One Sample t-test
data: cholesterin
t = 72.849, df = 7, p-value = 2.416e-11
alternative hypothesis: true mean is not equal to 0
95 percent confidence interval:
195.2014 208.2986
sample estimates:
mean of x
201.75 t.test(cholesterin, conf.level=0.99)
One Sample t-test
data: cholesterin
t = 72.849, df = 7, p-value = 2.416e-11
alternative hypothesis: true mean is not equal to 0
99 percent confidence interval:
192.0585 211.4415
sample estimates:
mean of x
201.75 # Daten übertragen
as.numeric(t.test(cholesterin, conf.level=0.90)$conf.int)[1] 196.5031 206.9969as.numeric(t.test(cholesterin, conf.level=0.95)$conf.int)[1] 195.2014 208.2986as.numeric(t.test(cholesterin, conf.level=0.99)$conf.int)[1] 192.0585 211.4415Die obere Grenze des 99%-Konfidenzintervall ist größer als 210. Wird dies berücksichtigt, lässt dich die Aussage nicht bestätigen.
52.6 Lösung zur Aufgabe 44.8.6
# Daten übertragen
a <- c(rep("geheilt", 18), rep("nicht", 7))
b <- c(rep("geheilt", 21), rep("nicht", 14))
freqA <- table(a)
freqB <- table(b)
A <- prop.test(freqA[["geheilt"]], sum(freqA),
alternative="two.sided",
p=0.5, conf.level=0.95)
B <- prop.test(freqB[["geheilt"]], sum(freqB),
alternative="two.sided",
p=0.5, conf.level=0.95)
# Konfidenzintervalle
A$conf.int[2] - A$conf.int[1][1] 0.3672662B$conf.int[2] - B$conf.int[1][1] 0.3343891Das Konfidenzintervall von Gruppe B ist schmaler, und damit auch präziser.
52.7 Lösung zur Aufgabe 44.8.7
# lade Datensatz
load(url("https://www.produnis.de/R/data/neonates.RData"))# t-Test
d <- t.test(neonates$weight, conf.level = 0.99)
# Konfidenzgrenzen
as.numeric(d$conf.int)[1] 2.975844 3.075531# t-Test
a1 <- t.test(neonates$apgar1, conf.level = 0.99)
a5 <- t.test(neonates$apgar5, conf.level = 0.99)
# Konfidenzgrenzen
as.numeric(a1$conf.int)[1] 5.422182 5.834068as.numeric(a5$conf.int)[1] 5.998597 6.426403Die Konfidenzgrenzen schneiden sich nicht. Das bedeutet, wir können von einem signifikanten Unterschied ausgehen.
# geringes Gewicht kategorisieren
neonates$GG <- "normal"
neonates$GG[neonates$weight<2.50001] <- "low"
# Subsets bilden
k1 <- subset(neonates, smoke=="Yes")
k2 <- subset(neonates, smoke=="No")
# Häufigkeitstabelle
freq1 <- table(k1$GG)
freq2 <- table(k2$GG)
# Proportion Test
m1 <- prop.test(freq1[["low"]], sum(freq1),
alternative="two.sided",
p=0.5, conf.level=0.95)
m2 <- prop.test(freq2[["low"]], sum(freq2),
alternative="two.sided",
p=0.5, conf.level=0.95)
# Konfidenzgrenzen anzeigen
as.numeric(m1$conf.int)[1] 0.1049334 0.2610870as.numeric(m2$conf.int)[1] 0.008396857 0.055169043Die Konfidenzgrenzen schneiden sich nicht. Das bedeutet, wir können von einem signifikanten Unterschied ausgehen.